内容如下:
1.外泌体和肝癌TCGA数据下载
2.数据格式整理
3.差异表达基因筛选
4.预后相关外泌体基因确定
5.拷贝数变异及突变图谱
6.外泌体基因功能注释
7.LASSO回归筛选外泌体预后模型
8.预后模型验证
9.预后模型鲁棒性分析
10.独立预后因素分析及与临床的相关性分析
11.列线图,ROC曲线,校准曲线,DCA曲线
12.外部数据集验证
13.外泌体模型与免疫的关系
14.外泌体模型与单细胞测序
########################### 4.预后相关外泌体基因确定 ############################
下面绘制森林图。
setwd("C:\\Users\\ASUS\\Desktop\\自噬")
dir()
rt <- read.table("uniCox_LTPM.txt",header=T,sep="\t",row.names=1,check.names=F)
rt <- rt[rt$pvalue<0.05,]
gene <- rownames(rt)
hr <- sprintf("%.3f",rt$"HR")
hrLow <- sprintf("%.3f",rt$"HR.95L")
hrHigh <- sprintf("%.3f",rt$"HR.95H")
Hazard.ratio <- paste0(hr,"(",hrLow,"-",hrHigh,")")
pVal <- ifelse(rt$pvalue<0.001, "<0.001", sprintf("%.3f", rt$pvalue))
n <- nrow(rt)
nRow <- n+1
ylim <- c(1,nRow)
layout(matrix(c(1,2),nc=2),width=c(3,2.5))
xlim = c(0,3)
par(mar=c(4,2.5,2,1))
plot(1,xlim=xlim,ylim=ylim,type="n",axes=F,xlab="",ylab="")
text.cex=0.8
text(0,n:1,gene,adj=0,cex=text.cex)
text(1.5-0.5*0.2,n:1,pVal,adj=1,cex=text.cex);text(1.5-0.5*0.2,n+1,'Pvalue',cex=text.cex,font=2,adj=1)
text(3,n:1,Hazard.ratio,adj=1,cex=text.cex);text(3,n+1,'Hazard ratio',cex=text.cex,font=2,adj=1,)
par(mar=c(4,1,2,1),mgp=c(2,0.5,0))
xlim = c(0,max(as.numeric(hrLow),as.numeric(hrHigh)))
plot(1,xlim=xlim,ylim=ylim,type="n",axes=F,ylab="",xaxs="i",xlab="Hazard ratio")
arrows(as.numeric(hrLow),n:1,as.numeric(hrHigh),n:1,angle=90,code=3,length=0.05,col="darkblue",lwd=2.5)
abline(v=1,col="black",lty=2,lwd=2)
boxcolor = ifelse((as.numeric(hr)>1)&(pVal<0.05),'red3',ifelse((as.numeric(hr)<1)&(pVal<0.05),"#36a8a9","black"))
points(as.numeric(hr), n:1, pch = 15, col = boxcolor, cex=1.3)
axis(1)
colors()
图片如下:
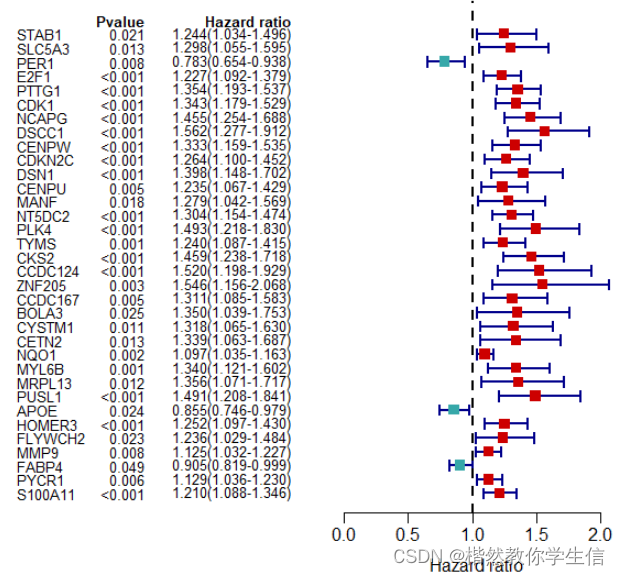
红色代表风险基因,绿色代表保护基因。
下一步绘制生存曲线。